BNSTS
Atvira kristalografinė duomenų bazė COD
Projektas COD [1] (nuo angl. Crytallography Open Database, http://www.crystallography.net/) siekia surinkti vienoje atviros prieigos duomenų bazėje visas publikuotas organinių, neorganinių ir metaloorganinių molekulių struktūras (išskyrus tik biologinių makromolekulių struktūras, kurias šiuo metu atvirai talpina PDB [2]).
Šią duomenų bazę įkūrė Armelis Lebe (Armel Le Bail), Lachlanas Kransvikas (Lachlan Cranswick), Michaelis Berntas (Michael Berndt), Luka Luterori (Luca Lutterotti) ir Robertas Dounsas (Robert M. Downs) 2003 vasaryje, atsakydami į Michaelio Bernto laišką SDPD elektroninio pašto grupėje (angl. Structure Determination by Powder Diffractometry mailing list) [3]. Nuo 2007 m. pagrindinis duomenų bazės serveris buvo perkeltas į Vilniaus Universiteto Biotechnologijos Institutą, kur jį prižiūri ir programinę įrangą vysto Saulius Gražulis ir Andrius Merkys. Šiuo metu COD duomenų bazė talpina virš 200 tūkst. įrašų, aprašančių struktūras, publikuojamas didžiausiuose recenzuojamuose kristalografijos ir chemijos žurnaluose [4]. Didžioji dalis duomenų apie mineralų struktūras į COD patenka iš AMCSD [5] duomenų bazės, juos COD pateikia AMCSD administratorius ir vienas iš COD įkūrėjų Robertas Dounsas.
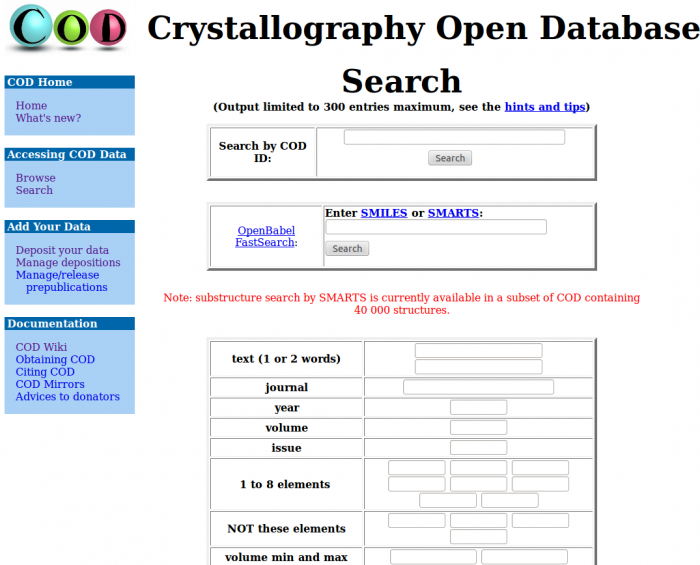
Duomenš bazės COD svetainė (Fig. a) atvirai prieinama internete ir leidžia ieškoti duomenų pagal pagrindinius kristalografinius ir cheminius parametrus (paieškos svetainę sukūrė Armelis Lebe ir Michaelis Berndtas), peržiūrėti surastas struktūras tiesiog naršyklėje (Fig. b) arba nusikelti jas į vietinį kompiuterį tolimesnei analizei. Be to, registruoti naudotojai gali įkelti į duomenų bazę naujas struktūras, tiek jau publikuotas mokslo spaudoje, tiek ruošiamas publikacijai ar pateikiamas kaip asmeniniai pranešimai COD. Įkėlimui naudojama programinė įranga, sukurta VU Biotechnologijos institute Sauliaus Gražulio, Justo Butkaus ir Andriaus Merkio. Įkėlimo svetainės programos griažtai patikrina įkeliamų duomenų sintaksę ir semantiką, taip užtikrindamos aukštą į COD patenkančių įrašų kokybę.
a)
b)
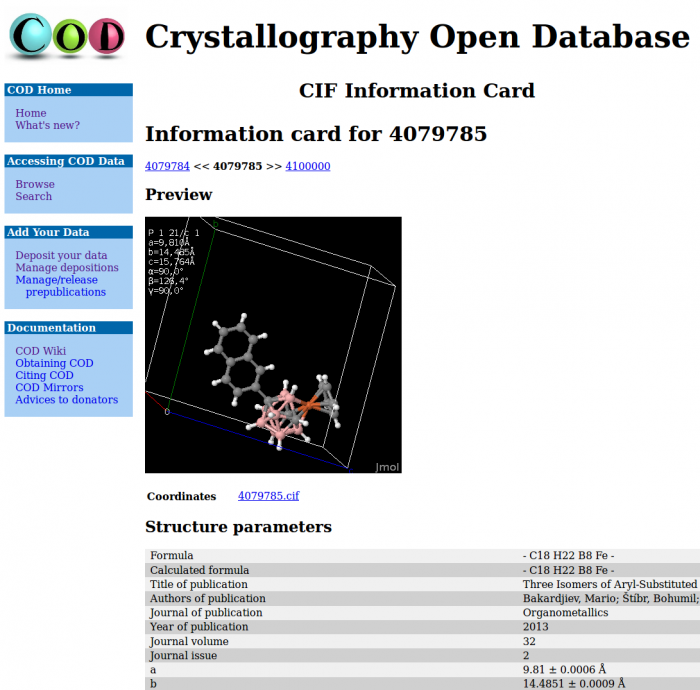
Fig. a) COD duomenų bazės žiniatinklio svetainė leidžia ieškoti kristalų struktūrų pagal jų kristalografinius, cheminius ir bibliografinius duomenis b) surastus duomenis galima peržiūrėti tiesiog naršyklės lange arba nusikelti tolimesniam apdorojimui, tiek pavienius įrašus, tiek visą surastą įrašų aibę.
Daug skaičiavimo resursų reikalaujančiai duomenų analizei COD duomenų bazės turinį galima nusikelti pilnai, naudojant Subversijos, Rsync ar HTTP protokolus. Paprastas ir atviras priėjimas prie COD duomenų paskatino įvairius šios duomenų bazės panaudojimus, ji naudojama programinei įrangai testuoti [6], mokymo tikslams [7] bei moksliniams tyrimams [8].
Atviras COD duomenų bazęs pobūdis leido sukurti visą eilę COD antrinių serverių ("veidrodinių") skirtingose žemės rutulio vietose [9-12], bei paruošti specialiems tikslams pritaikytus COD duomenų bazės variantus [7]. Šiuo metu duomenų bazė COD yra pilniausias atviras žiniatinklio resursas, leidžiantis Lietuvos ir viso pasaulio mokslininkams prieiti prie struktūrinės informacijos apie mažas molekules.
Nuorodos
1. Gražulis, S.; Chateigner, D.; Downs, R. T.; Yokochi, A. F. T.; Quirós, M.; Lutterotti, L.; Manakova, E.; Butkus, J.; Moeck, P. & Le Bail, A. (2009). Crystallography Open Database - an open-access collection of crystal structures, Journal of Applied Crystallography 42 : 726-729.
2. Berman, H.; Henrick, K. & Nakamura, H. (2003). Announcing the worldwide Protein Data Bank, Nat Struct Mol Biol 10 : 980-980.
3. Berndt, M. (2003). Open crystallographic database - a role for whom?, http://tech.groups.yahoo.com/group/sdpd/message/1016 (retrieved 2013.01.31).
4. Gražulis, S.; Daškevič, A.; Merkys, A.; Chateigner, D.; Lutterotti, L.; Quirós, M.; Serebryanaya, N. R.; Moeck, P.; Downs, R. T. & Le Bail, A. (2012). Crystallography Open Database (COD): an open-access collection of crystal structures and platform for world-wide collaboration, Nucleic Acids Research 40 : D420-D427.
5. Rajan, H.; Uchida, H.; Bryan, D.; Swaminathan, R.; Downs, R. & Hall-Wallace, M. (2006). Building the American Mineralogist Crystal Structure Database: A recipe for construction of a small Internet database. In: Sinha, A. (Ed.), Geoinformatics: Data to Knowledge, Geological Society of America.
6. Grosse-Kunstleve, R. & Gildea, R. (2011). Computational Crystallography Initiative: COD stats, http://cci.lbl.gov/cod_stats/ (retrieved 2013.01.31).
7. Moeck, P. (2004). EDU-COD: Educational Subset of COD, http://nanocrystallography.research.pdx.edu/search/edu/ (retrieved 2013.01.31).
8. First, E. L. & Floudas, C. A. (2013). MOFomics: Computational pore characterization of metal-organic frameworks, Microporous and Mesoporous Materials 165 : 32-39.
9. Quirós-Olozábal, M. (2006). COD Mirror of Granada University, http://qiserver.ugr.es/cod/ (retrieved 2013.01.31).
10. Moeck, P. (2007). Crystallography Open Database Mirror, http://nanocrystallography.research.pdx.edu/search/codmirror/ (retrieved 2013.01.31).
11. Gražulis, S. (2007). COD Mirror in Vilnius, http://cod.ibt.lt/ (retrieved 2013.01.31).
12. Chateigner, D. (2010). Crystallography Open Database Mirror at ENSICAEN, http://cod.ensicaen.fr/ (retrieved 2013.01.31).
CRISPR
CRISPR/Cas sistemų struktūros ir molekulinių mechanizmų tyrimai
Neseniai atrasta nauja bakterijų apsaugos nuo bakteriofagų ir plasmidžių DNR sistema CRISPR (angl. "Clustered regularly interspaced short palindromic repeats") veikia panašiai kaip eukariotinių organizmų imuniteto sistema. CRISPR sistemos yra plačiai paplitusios ir randamos tiek prokariotiniuose organizmuose, tiek archėjose. CRISPR sritį genome sudaro trumpi (21- 49 bp ilgio) dalinai palindrominiai DNR pasikartojimai (gali būti nuo 2 iki 250 pasikartojimų). Tarp pasikartojančių DNR sekų yra įsiterpusios unikalios DNR sekos "skirtukai (angl. spacers)" kurie būna 20-58 bp ilgio. šalia CRISPR srities genome yra išsidėstę Cas (CRISPR-associated) genai (nuo 3 iki 10), kurią koduojami baltymai dažnai turi funkcinius domenus, būdingus nukleazėms, helikazėms, polimerazėms ir kt. su nukleorūgštimis sąveikaujantiems baltymams.
CRISPR/Cas sistema suteikia šeimininko ląstelei atsparumą bakteriofagams ir kitai "svetimai" nukleorūgščiai. Bakteriofagui ar plazmidei patekus į ląstelę, kai kurios bakterijos sugeba įsistatyti į savo genomą naujus skirtukus, kurie yra identiški bakteriofago ar plazmidės DNR sekoms. Tokios pasikeitusios bakterijos įgyja atsparumą tam fagui ar plazmidei, kurio DNR fragmentus jos įsistatė į savo genomą. Šio reiškinio molekuliniai mechanizmai kol kas neišaiškinti. Nežinoma, nei kaip atpažįstama "svetima" bakteriofago ar plazmidės DNR, nei kaip įsistatomas naujas skirtukas, nei kaip jis parenkamas. Šie mechanizmai yra tiriami mūsų skyriuje.
Projektai
Baltymų-nukleorūgščių sąveikos tyrimų skyrius
 | Skyriaus vedėjas:
Tel. +370-5-2234354 | Mokslo darbuotojai(-os): Dr. Giedrius Gasiūnas Dr. Saulius Gražulis Dr. Tautvydas Karvelis Dr. Elena Manakova Dr. Andrius Merkys Dr. Giedrius Sasnauskas Dr. Arūnas Šilanskas Dr. Tomas Šinkūnas Dr. Giedrė Tamulaitienė Dr. Gintautas Tamulaitis Dr. Paulius Toliušis Dr. Mindaugas Zaremba Dr. Evelina Zagorskaitė Dr. Marijonas Tutkus Dr. Nina Urbelienė Dr. Danielis Rutkauskas Dr. Marija Jankunec Dalia Smalakytė, MSc Inga Songailienė, MSc Gediminas Drabavičius, MSc Rimantė Žedaveinytė, MsC Lina Aitmanaitė, MSc Rūta Zinkevičiūtė, MSc Doktorantai(-ės): Greta Bigelytė, MSc Gediminas Drabavičius, MSc Edvardas Golovinas, MSc Irmantas Mogila, MSc Antanas Vaitkus, MSc Dalia Smalakytė, MSc Donata Dakinevičien,ė MSc Algirdas Grybauskas, MSc Gediminas Drabavičiu,s MSc Jonas Juozapaitis, MSc Studentai(-ės): Simonas Ašmontas Konstantyj Keda Danas Klimavičius Aurimas Kopūstas Eglė Kupčinskaitė Danguolė Norkūnaitė Džiugas Sabonis Rugilė Ivanickaitė Ugnė Gaižauskaitė Tomas Venclovas Gytis Druteika Aistė Petrauskaitė Karolis Sabutis Justė Paksaitė Ugnė Tylenytė Marija Duchovskytė Laborantai(-ės): Ana Tunevič Jadvyga Matulevič Ilinykh |
 | ||
Bendra tyrimų apžvalga | ||
Visos gyvybės formos nuo bakterijų iki žinduolių yra potencialūs virusų taikiniai. Bakterijų virusai (bakteriofagai) gali sunaikinti ištisas bakterijų populiacijas. Evoliucijos eigoje bakterijos sugebėjo išlikti sukurdamos gynybos sistemas, kurios saugo ląsteles nuo bakteriofagų ir svetimų nukleorūgščių patekimo. Kadangi bakteriofagai gali daugintis tik ląstelėje, jie kinta, ieškodami būdų kaip įveikti ląstelių gynybos barjerus, o bakterijos priverstos kurti naujas apsaugos sistemas.
Daug žmogui naudingų produktų, pvz., pieno produktai, bioaktyvūs junginiai ir vaistai, yra gaminami panaudojant bakterijas. Tokioje gamyboje bakteriofagų infekcijos yra labai pavojingos, kadangi jos gali sunaikinti visą bakterijų populiaciją, todėl pramonėje yra reikalingi bakterijų kamienai, turintys efektyvias antivirusinės apsaugos sistemas. Norint sukurti tokius bakterijų kamienus laboratorijoje, reikia suprasti, kaip veikia antivirusinės apsaugos sistemos.
Mūsų skyrius tiria fermentus ir jų kompleksus, kurie yra atsakingi už bakterijų apsaugą nuo svetimų nukleorūgščių. Labiausiai mus domina restrikcijos endonukleazių bei CRISPR molekulinio aparato struktūra ir veikimo mechanizmas. Tyrimams naudojame rentgenostruktūrinę analizę, mutagenezę, biocheminius ir biofizikinius tyrimo metodus.
Projektai
![]() CRISPR
CRISPR
![]() Restrikcijos endonukleazės
Restrikcijos endonukleazės![]() COD
COD











 2017 - 2018
2017 - 2018